| 차세대 게놈 시퀀싱 기술인 NGS
(next generation sequencing)가 매일 좋아 지고 있어서 한 사람의 전체
유전체를 시퀀싱을 하는데 하루(1 day)에 가능하고 이러한 결과를 고급 분석하는 것도 하루(1 day)에 가능하게 되었다.
또한, 가격이 급격하게 하락을 해서 1명의 인간게놈 시퀀싱을 하는데 드는 비용이 $1,000에 근접하고 있다. 그리고, 차세대
고집적 병렬계산용 프로세서(GPU)인 테슬러 계열인 페르미는 현재는 448개의 cores가 한장의 카드에 집적이 되었고
연산능력이 1,000 GFlops를 넘나들고 있다. 이러한 2개 다른 과학제 분야의 차세대 기술의 만남의 성과로 GPU에 기반한 게놈어셈블러 Soap3-GPU(HKU, 홍콩)와 단백질 시뮬레이터 Amber-GPU (UCSF, 미국)가 최근에 과학적인 새로운 돌파구가 되고 있다. 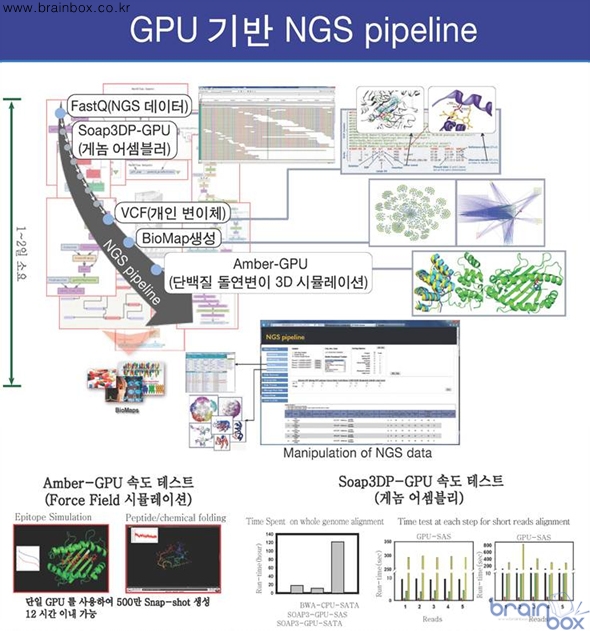 Soap3-GPU는 BWT알고리듬을 사용하는데 GPU가 이러한 단순한 알고리즘의 반복적인 연산에 적합한 환경을 가지고 있기 때문에 최적화/실용화가 가능해졌고 한국에서는 nVidia 바이오 파워채널 회사인 (주)신테카바이오가 자체적으로 GPU에 설치 및 최적화 테스트를 국내에서 처음으로 완료하였다고 발표하였다. 위의 툴을 사용하면 정상 CPU에 비해 테슬러 페르미 C2075모델 GPU에서는 10~20배 빠르고, GPU Device와 CPU의 초고속 스토리지(SAS)를 최적화 하면 추가적으로 10배 빨라져서 GPU와 초고속 스토리지 조합으로 최고 100배의 속도 효과를 기대 할 수 있다. 또한, Amber시스템은 오랜 전통의 미국UCSF에서 개발한 단백질 시뮬레이션을 하는 패키지이고 설치가 극히 까다로운데 최근 Amber12-GPU를 한국에서는 최초로 (주)신테카바이오가 GPU환경에 설치 및 다양한 응용(버추얼스크리닝, 도킹 및 컴플랙스 모델링)에 대한 테스트를 성공적으로 완료했다고 밝혔다. Amber12-GPU 툴을 사용하면 정상 CPU에 비해 GPU에서는 10~20배 빠르고 정상적으로 하루밤 (12시간)에 약 500만 모션 스냅샷을 만들어 낼 수 있고 항원-항체 시뮬레이션은 이미 실용화가 가능하다고 밝혔다. 한국과학기술연구원 벤처센터에 위치한 (주)신테카바이오는 최근 이러한 Amber12-GPU 와 Soap3DP-GPU를 묵어서 차세대 시퀀싱에서 단백질 시뮬레이션까지의 최적화 환경의 초기버전 파이프라인으로 개발 완성 하였고 테스트를 끝마쳤고 7월 초부터 본격 서비스를 시작한다고 코엑스 2012 코리아그래픽월드 및 일본 도쿄빅사이트(BioTech2012)에서 동시에 발표하였다. |
이러한 2개 다른 과학제 분야의 차세대 기술의 만남의 성과로 GPU에 기반한 게놈어셈블러 Soap3-GPU(HKU,
이 기사가 마음에 드셨다면 공유해 주세요
- 만우절 실수? 스태퍼 케이스 외전 '다이스 이터' 무료 전환
- 한국적 요소 가미, ‘수일배’ 진승호 신작 개발자 모집 중
- 中 우체국 컬래버 논란, 스노우 브레이크 한 달째 점검
- 엘든 링 오케스트라 공연, 4월 6일 2차 티켓 오픈한다
- 스팀게임을 패키지로 전시, 방 꾸미기 신작 ‘박스룸’ 공개
- 출시 12일 만에, 붉은사막 판매량 400만 장 돌파
- 25년 만에 재출시, 토막: 지구를 지켜라 에픽서 무료 배포
- 시프트업, '바하 아버지' 미카미 신지의 개발사 인수
- 닌텐도 ‘팰월드’ 소송 빨간불, 미국서 핵심 특허 거절 판정
- 사이버펑크 TCG, 킥스타터 역사상 최대 규모 후원액 달성
게임일정
2026년
04월
| 일 | 월 | 화 | 수 | 목 | 금 | 토 |
|---|
인기게임순위
-
1
 리그 오브 레전드
리그 오브 레전드
-
2
 리니지
리니지
-
3
 발로란트
발로란트
-
4
 FC 온라인
FC 온라인
-
51
 아이온2
아이온2
-
63
 오버워치(오버워치 2)
오버워치(오버워치 2)
-
72
 플레이어언노운스 배틀그라운드
플레이어언노운스 배틀그라운드
-
8
 서든어택
서든어택
-
93
.jpg) 던전앤파이터
던전앤파이터
-
103
.jpg) 메이플스토리
메이플스토리